基本介紹
- 中文名:二級結構
- 外文名:secondary structure
- 學科:生化
- 含義:生物巨分子
概述,詳細信息,編號,蛋白質,核酸,二級結構,比對,
概述
詳細信息
由於氫鍵與其他結構特徵有所關聯,所以它所定義的二級結構會稍為不正式。就如蛋白質螺旋,在拉曼強傳標繪圖的特定區域,通常會採用主鏈二面角。這樣,以這個二面角的區段都會被稱為“螺旋”,而不論它是否真正的氫鍵。其他稍為不正式的定義亦有被建議,且是多是套用曲線微分幾何的觀念,如曲率及扭量。而最不正式的,要算是結構生物學定以肉眼來決定及紀錄原子量級的二級結構。
對生物巨分子的二級結構可以初步以光譜來估計。對於蛋白質可以用一種普遍的方法稱為長紫外線(波長170-250nm)圓二色譜。在雙最小的208nm及222nm可以顯示α螺旋結構,而單最小的204nm或207nm則分別可以顯示任意形或β摺疊結構。一個較少用的方法是紅外線光譜,它可以偵測因氫鍵所造成胺基的震盪。最後,二級結構可以準確地以核磁共振的化學位移來估計。
編號
DSSP是“Define Secondary Structure of Proteins”的縮寫,它是一編文章正式列出已知三維結構的蛋白質二級結構。DSSP編號一般是用單一英文字母來描述蛋白質二級結構。二級結構是根據氫鍵模式來指定的。
* G:3轉角螺旋(亦即310螺旋)。最短長度為3個殘基。
* H:4轉角螺旋(α螺旋)。最短長度為4個殘基。
* I:5轉角螺旋(π螺旋)。最短長度為5個殘基。
* T:氫鍵轉角(3、4或5個轉角)。
* E:平行的β摺疊,或/及反平行的摺疊形態(延伸鏈)。最短長度為2個殘基。
* B:獨立β橋內的殘基(一對β摺疊氫鍵)
* S:彎曲(唯一非氫鍵的指定)
所有不是以上形態的殘基,在DSSP都是以空格來指定的,而有時則以C來代表捲曲或L來代表環。螺旋(即G、H及I)及摺疊形態都需要一定的長度。這即是指兩個在一級結構鄰接的殘基必須形成相同的氫鍵模式。如果螺旋或摺疊的氫鍵模式太短,就會分別以T或B來編碼。當中亦有其他蛋白質二級結構編號,但卻較少使用。
蛋白質二級結構預測
早期蛋白質二級結構預測的方法是建基於胺基酸形成螺旋或摺疊的傾向,而有時須聯同估計形成二級結構的能量的方法來使用。這些方法在預測殘基的三種狀態(螺旋、摺疊或捲曲)可以有約60%的準確性,若使用多序列比對可以將準確性大幅提升至80%。多序列比對可以知道胺基酸在某一位置的完正分布(包括在其附近的位置,一般在每一邊的7個殘基),而演化過程提供了結構趨向更明確的圖畫。例如,在蛋白質某位置的甘胺酸,本身已表明那是一個任意形。但是多序列對比可以發現,在接近十億年演化後95%的蛋白質中,那是一個有利螺旋的胺基酸。再者,若在那位置檢測平均疏水性,亦會發現其殘基可溶性是與α螺旋一致。綜合來說,這些因素顯示原先蛋白質內甘胺酸是α螺旋結構,而非任意形。多種方法都會結合已有的數據來組成三種狀態的預測,這些方法有神經網路、隱馬爾可夫模型及支持向量機。現代預測方法亦可在每一個位置的預測結果提供信賴分數。
二級結構預測方法一直不斷地在校準,例如EVA實驗。基於約270個星期的測試,最準確的方法要算是PsiPRED、SAM、PORTER、PROF及SABLE。有趣的是,在這多種方法中找出共識或一致,並不能提升它們的準確性。最大改善的地方似乎是在β股的預測,因為所使用的方法會忽視一些β股段。整體上而言,最高的預測準確性只可以達90%,因DSSP的標準方法的性質,與校準的預測相違背。
蛋白質
蛋白質的二級結構包含局部殘基之間由氫鍵所調節的相互作用。最普遍的二級結構就是α-螺旋及β-摺疊,此外還有β-轉角和無規捲曲。經計算後發現其他螺旋,例如310螺旋及π螺旋,在能量上有著有利的氫鍵模式,但這些螺旋卻是在自然的蛋白質中是很稀有的,要α螺旋在中央進行不利的骨架包裝後,才可在末端中發現。緊的轉角、鬆開及靈活的環會連結更多“規則的”二級結構。任意形並非真正的二級結構,但卻是一類缺乏規則的二級結構的形態。
胺基酸在形成不同的二級結構上有著不同的能力。脯氨酸及甘氨酸會在轉角上出現,並且可以瓦解α螺旋骨架的規則形態,但兩者卻有著不正常的形態能力。在蛋白質內採用螺旋形態的胺基酸有蛋氨酸、丙氨酸、亮氨酸、谷氨酸及賴氨酸(胺基酸單字母編號為“MALEK”);相反,大型的芳香性殘基(色氨酸、酪氨酸及苯丙氨酸)及Cβ分枝的胺基酸(異亮氨酸、纈氨酸及蘇氨酸)則採用β摺疊形態。但是,若單以序列來看,這些都不足以構成一個可靠的方法來預測二級結構。
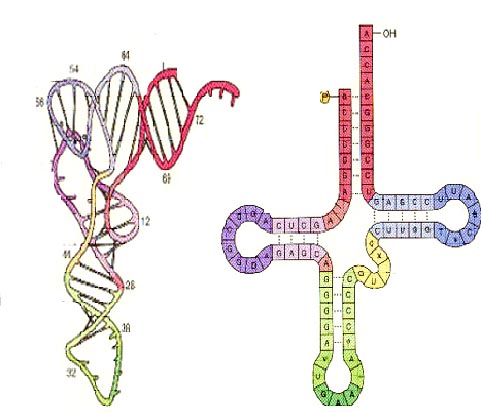
核酸
核酸亦有二級結構,大部份都是單股核糖核酸(RNA)分子。RNA二級結構可以分為螺旋(緊接的鹼基對)及不同種類的環(被螺旋圍繞的不成對核苷酸)。莖環結構是一個鹼基對螺旋結構,末端為短少的不成對環。這種莖環結構非常普遍,並且是建構大型結構基元,如三葉草結構(即如在轉運RNA中的四個螺旋結點)的基本單位。內環結構(在長鹼基對螺旋中的短而不成對鹼基)及膨出(在螺旋股中額外插入,但卻在相對股中沒有配對的鹼基)亦很經常會出現。最後,偽結及base triples亦會出現在RNA。
由於RNA二級結構差不多全都是由鹼基對作為中介,它可以說是確定在一個分子或複合物中哪些鹼基成對。但是,傳統的華生—克里克鹼基對並非唯一在RNA的配對方法,霍氏配對方法亦很普遍。
二級結構
生物信息學的其中一種套用是使用預測的RNA二級結構來搜尋用作RNA功能形式而非編碼的基因組。舉例來說,小分子RNA有著由小內環中斷的長莖環結構。計算可能的RNA二級結構可以用動態規劃方法,但是它不能偵測出偽結或是其他鹼基對沒有全面網羅的情況較通用的方法有隨機上下文無關語法。Mfold是一個使用動態規劃的網站。